Plateforme de Transcriptomique Plante de Paris-Saclay, POPS
Présentation
La plateforme de transcriptomique des Plantes de Paris Saclay (POPS) propose depuis 2003 des services d’analyse du transcriptome des plantes à la communauté scientifique académique ou industrielle nationale ou internationale. Composée de techniciens, de biologistes, de bio-informaticiens et de statisticiens, elle est hébergée par l’Institut de Science des Plantes de Paris-Saclay sur le plateau de Saclay.
La plateforme POPS a pour mission de mutualiser des équipements, des compétences, des outils et des services afin de les proposer à une communauté scientifique publique ou privée, offrant ainsi une expertise forte et une offre intégrée dans le domaine de la transcriptomique végétale.
Les 3 axes de la plateforme transcriptomique sont :
- Service intégré à façon
- Développement
- Formation et animation scientifique
Elle est labellisée IBiSA et Infrastructure Scientifique Collective par INRAE. Elle fait partie du Réseau France Génomique et elle est certifiée ISO9001 depuis 2013.
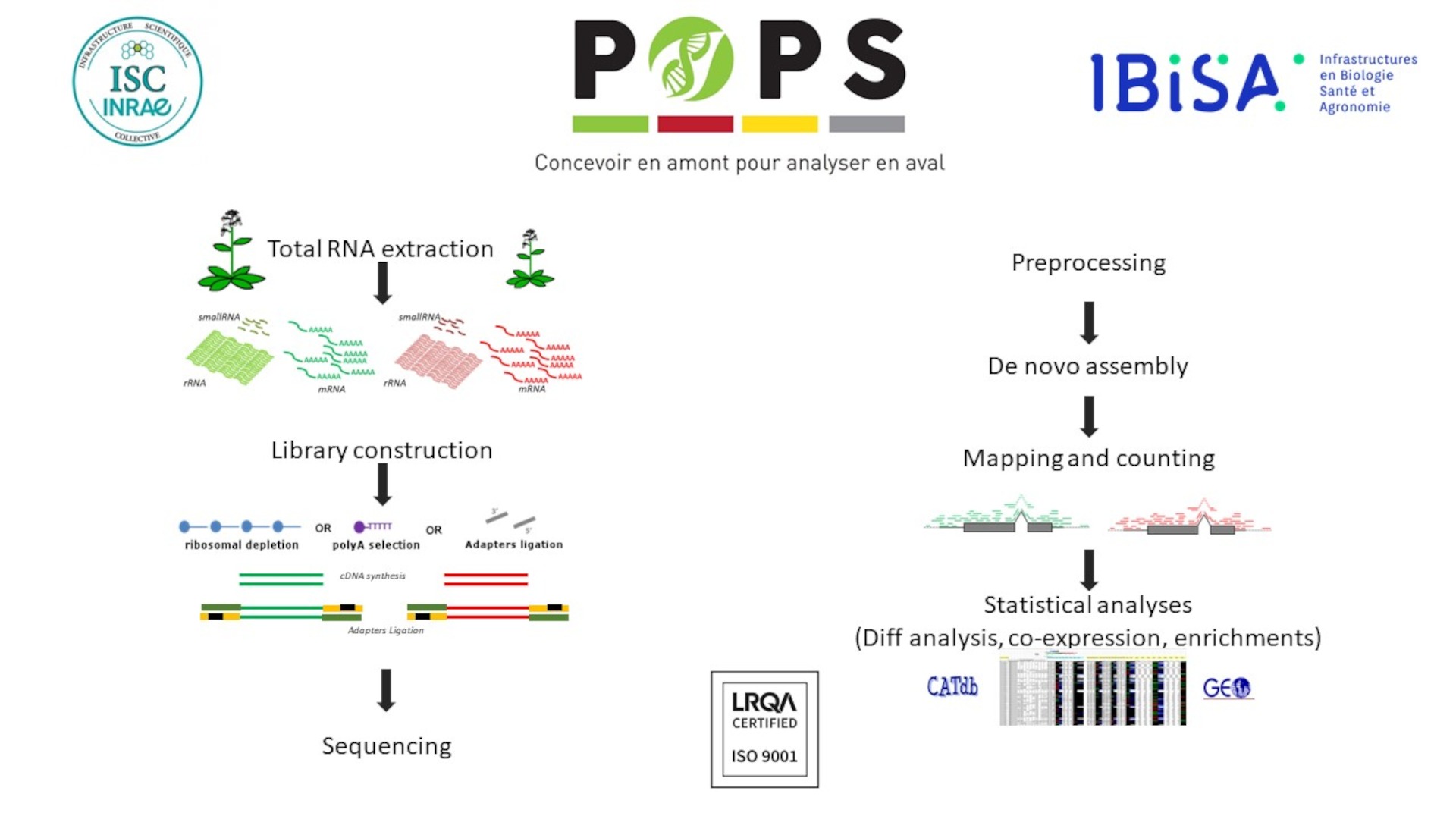
Activités
Expertises
La plateforme transcriptomique POPS réalise des projets d’étude du transcriptome en collaboration avec des équipes de recherche nationales et internationales. Elle offre une expertise pour l’analyse de l’expression comparative des gènes par l’utilisation du séquençage à haut débit de l’ARN, ou RNA-seq. Cette offre est complétée par l’analyse bio-informatique et statistique des données brutes permettant l’étude quantitative du transcriptome.
- Conception du projet en interaction avec le collaborateur (technologie, planification, …).
- Réalisation technique et production des données RNAseq.
- Analyses bio-informatiques et statistiques adaptées pour fournir des résultats exploitables.
- Interprétation des résultats.
- Prise en charge de la soumission dans les bases de données.
Points forts
- Versatilité : Diversité des organismes, Pluralité d’échantillons (type de culture, type d’organes, tissus …). Adaptabilité au nombre d’échantillons (test, moyen et haut débit).
- Interlocuteur dédié pour votre projet.
- Pipelines d’analyses bioinformatiques et statistiques développés spécifiquement pour nos applications.
Equipements
- bioanalyzer
- Fragment Analyzer
- Covaris
- Clariostar
- robot pipeteur Biomek FX
- Illumina NextSeq500
- Accès aux séquenceurs Illumina NovaSeq du CNS (Evry)
- Nanopore P2 solo
- cluster de calcul
Services proposés
Applications proposées
- Séquençage orienté des ARN polyAdenylés (le brin codant).
- Séquençage non orienté des ARN polyAdenylés.
- Séquençage des petits ARN : miRNA, siRNA …
- Séquençage de longs fragments (projets collaboratifs)
- Séquençage orienté des ARN non polyAdenylé (déplétion).
- Microtranscriptomique ou séquençage de très faible quantité d’ARN (à partir de 75pg d’ARN total).
- Métatranscriptomique ou séquençage du transcriptome de plusieurs espèces à partir d’un même échantillon.
- Empreintes.
- Cellule unique : en cours de développement.
Protocoles personnalisables en fonction de besoins spécifiques.
Options de séquençage
- Séquenceur NextSeq 500
- Accès aux séquenceurs HiSeq (CEA-CNS, Evry)
- Single Read ou Paired-End
- Longueurs de séquençage : 75, 100, 150 bases
Analyses bioinformatiques et statistiques
- Mapping
- Analyse différentielle de gènes
- Assemblage
- Traitement des smallRNA
Autres analyses possibles en collaboration avec l’équipe Réseaux Génomiques
Thématiques
Contact
Plateforme de Transcriptomique des Plantes de Paris-Saclay
Bâtiment 630, plateau du Moulon
Avenue des Sciences
91190 Gif-sur-Yvette
pops.ips2@universite-paris-saclay.fr
Site web
Tutelles
Université Paris Cité, Université Paris Saclay, Université Evry val d’Essonne, CNRS, INRAE
Unité de rattachement
Institut des Sciences des Plantes de Paris Saclay – UMR 9213
Réseaux
France Génomique
Labellisation
IBiSA, ISC
Certification
Norme ISO 9001
Plateformes dans la même thématique
Plateforme Synthèse Chromatographie et RMN (SynChroR)
La plateforme Synthèse Chromatographie et RMN est hébergée au sein du Laboratoire ITODYS et 3 pôles : la synthèse , la chromatographie et la spectroscopie par résonance magnétique nucléaire (RMN)
Plateforme Proteom’IC 3P5
Proteom’IC est la plateforme d’analyses protéomiques par spectrométrie de masse de l’Institut Cochin localisée au sein de l’hôpital Cochin
enSCORE (engineered Spinal and Cortical Organoid coRE”)
enSCORE propose un support technique et scientifique aux chercheurs pour la génération de modèles organoïdes neuraux (spinaux et corticaux) dérivés de cellules souches pluripotentes induites humaines
Chromatographie analytique et préparative – CAP 42
Le plateau technique CAP42 permet de réaliser des extractions, des analyses chromatographiques et des purifications de substances qui peuvent être d’origine naturelle ou synthétique.
Plateforme d’imagerie moléculaire (iMAP) du CRI
iMAP (ion MAP) est une plateforme d’imagerie par spectrométrie de masse (MSI) qui propose son expertise et des expérimentations sur tissus congelés ou fixés en paraffine pour des analyses de protéomique, lipidomique ou glycomique
Plateformes de l’IBPC
L’institut de Biologie Physico-Chimique (IBPC) est fidèle à sa vocation pluridisciplinaire de promouvoir des recherches dans tous les domaines de la Biologie.
Plateforme d’expertise technologique de Production, d’Ingénierie, et de Caractérisation de Vésicules Extracellulaires pour des Thérapies Personnalisées (IVETh)
La plateforme a pour objectif d’offrir des expertises autour des vésicules extracellulaires et un parc d’équipements de rupture pour la caractérisation du sécrétome et des vésicules extracellulaires thérapeutiques ou issues de biofluides pour du diagnostic.
Cette plateforme est ouverte à la communauté scientifique académique et industrielle.
Plateforme de Biochimie & Biophysique (B&B) de l’IPNP
La plateforme de Biochimie et Biophysique (B&B) de l’Institut de Psychiatrie et Neurosciences de Paris (IPNP) est dédiée à la purification et l’analyse des protéines (natives ou recombinantes), la caractérisation des interactions protéine-protéine et protéine-lipide, et la production d’acides nucléiques (vecteurs ADN, ARNm).
